2023年7月12日,中国科学院生物物理研究所薛愿超团队在《Nature》杂志在线发表了题为"Complementary Alu sequences mediate enhancer-promoter selectivity"的研究论文。
转录调控在维持细胞功能和正常发育过程中起着关键作用。其中,增强子(enhancer)作为调控基因转录的重要元件,往往需要通过远距离染色质环化与目标启动子(promoter)相互作用,从而决定基因的时空表达特异性。这一过程不仅参与了细胞命运的决定,还在多种疾病的发生发展中扮演着重要角色。增强子能够精确地选择需要激活的目标启动子,以准确调节特定基因的转录时间和转录水平。然而,增强子和启动子配对选择的特异性是如何实现的依然是未解之谜。
为了解决这一关键科学问题,薛愿超团队利用实验室之前开发的RNA原位构象测序技术RIC-seq(Nature, 2020),系统捕获了增强子RNA(eRNA)和启动子来源的非编码RNA(uaRNA或 PROMPTs)之间的相互作用,并构建了高分辨率增强子-启动子RNA互作(EPRI)图谱。与传统的染色质构象捕获技术如Hi-C、HiChIP、ChIA-PET等不同,RIC-seq技术可直接鉴定增强子和启动子非编码RNA之间的空间互作位点,并据此推导增强子-启动子的链接网络,因此在解析增强子-启动子互作的序列特征方面具有更高的分辨率。
基于EPRI图谱,该研究团队发现增强子与启动子之间的配对选择特异性受到基因组重复序列Alu的调控。Alu序列是哺乳动物尤其是人类基因组中广泛分布的重复元件。研究人员发现,增强子和启动子RNA中的Alu序列充当了增强子-启动子之间相互交流的中介,并通过多种实验证明增强子RNA和启动子RNA中反向互补的Alu序列可通过碱基配对形成RNA双链,从而决定了增强子-启动子的配对选择特异性。这一发现不仅揭示了Alu在基因表达调控中的新机制,还为理解增强子和启动子非编码RNA在转录激活的功能提供了新视角。
此外,研究人员通过将非编码区突变映射到增强子-启动子RNA互作(EPRI)图谱,构建了"突变-功能"图谱,系统地注释了非编码突变(尤其是Alu元件的删除和插入)影响的靶标基因,为理解疾病发生提供了宝贵的资源。研究团队进一步发现,位于Alu元件中的突变可能会影响众多蛋白质编码基因的转录,从而对细胞命运产生重要影响。如癌基因PTK2增强子中的多态性Alu元件删除能够显著降低癌细胞增殖和侵袭能力,这为Alu元件突变与癌症易感性之间的关联提供了重要线索。
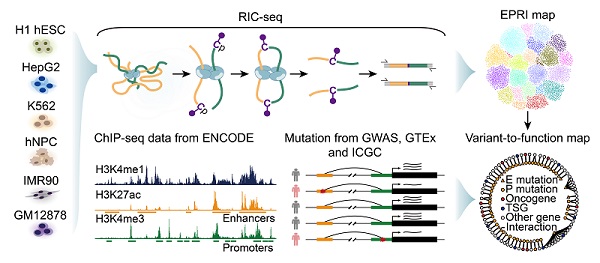
"增强子-启动子互作图谱"以及"突变-功能图谱"构建
该研究工作从非编码RNA的角度上揭示了增强子-启动子配对选择特异性的原则,并将非编码风险变异与其分子功能联系了起来,为我们深入理解基因转录调控的分子机制,以及疾病发生发展提供了新范式。
该项工作得到了国家重点研发计划、国家自然科学基金委、中科院先导项目和王宽诚教育基金等多项基金资助。中国科学院生物物理所博士后梁良,副研究员曹唱唱、吉蕾,特别研究助理蔡兆奎为本文共同第一作者,薛愿超研究员为唯一通讯作者。河南师范大学硕士研究生王若言和白志博参与了该项研究工作。该研究工作还得到了广东省人民医院朱平教授和河南师范大学杨献光教授的帮助和指导。此外,生物物理所生物成像平台和实验动物平台也为该研究提供了技术支持。
文章链接:https://www.nature.com/articles/s41586-023-06323-x
(供稿:薛愿超研究组)
 附件下载:
附件下载: